Olá pessoal, tudo bem com vocês??
Para quem tem acompanhado nosso blog sabe que vimos a teoria da biologia molecular. Esse conhecimento é necessário para a compreensão da aplicabilidade das técnicas de biologia molecular.
Vamos aprender sobre??
A utilização das técnicas de biologia molecular permite o estudo do genoma completo ou de sequências específicas do DNA, de sequências longas ou curtas, com o objetivo de detectar e analisar as sequências de interesse, que podem ser uteis para analise forense, diagnóstico clínico, ciências agronômicas, e pesquisa básica, translacional e aplicada.
As seguintes técnicas são adotadas pela confiabilidade, rapidez, especificidade, e flexibilidade, quando comparado a outros métodos.
Para dar início a qualquer técnica da biologia molecular a primeira etapa é a obtenção desse material genético…
Vamos conferir?
Extração de DNA e RNA
Hoje pode obter o material genético de uma variedade de tecidos, esses estudos requerem uma fonte confiável de material biológico genético para análise molecular, porém por conta da baixa disponibilidade do DNA ou RNA essas análises podem ser restritas.
Um dos principais obstáculos a serem superados em estudos é conseguir uma amostra com quantidade e qualidade de DNA. Os procedimentos para obter esse material genético têm que garantir o rompimento da célula de maneira que não promova a degradação desse material genético.
Então, substâncias como potencial detergente, para auxiliar no rompimento da bicamada lipídica são utilizadas; Enzimas que irão promover a retirada de proteínas e/ou RNA a depender se estivermos obtendo DNA (como proteinases, RNAses); substancias para conferir purificação e eluição desse material genético são essenciais.
No caso do RNA por ser uma molécula delicada devido a presença de uma hidroxila (OH) no carbono 2, na ribose habilita o RNA como nucleófilo, tornando-o vulnerável à degradação enzimática (1).
O RNA também tem um alto grau de suscetibilidade a metabólitos secundários (2) e, às vezes, moléculas inibitórias co-precipitadas durante o processo de extração de RNA podem interferir nas reações enzimáticas subsequentes (3, 4).
Dada a importância da qualidade do RNA para a pesquisa de expressão gênica, diversos estudos são realizados para ajustar os métodos de extração de RNA (4, 5) precisam ser investigados e adaptados se necessário (6), uma vez que amostras de qualquer material genético de baixa qualidade comprometem necessariamente todas as análises subsequentes, representando perda de tempo e recursos de pesquisa.
Para o processo de extração existem inúmeras metodologias, kits comerciais que visam melhorar a qualidade do processo de extração.
O sucesso no processo de extração do material genético deve ser medido em função da quantidade, qualidade e integridade do produto extraído (4).
Para isso análises posteriores as etapas de extração são necessárias para quantificar e verificar a integridade do mesmo.
Enzimas de restrição
Uma das técnicas que podem ser utilizadas pós extração de DNA é o uso de enzimas de restrição.
O que são enzimas de restrição?
Uma enzima de restrição é uma enzima que corta DNA em locais específicos no DNA. Muitas enzimas de restrição fazem cortes escalonados no local de seus sítios de reconhecimento ou perto deles, produzindo terminações de fita simples.
As enzimas de restrição fazem parte da defesa das bactérias aos invasores, essas bactérias na presença de invasores produzem enzimas que possuem sítios de restrição no DNA exógeno que levam a clivagem e eliminação do mesmo.
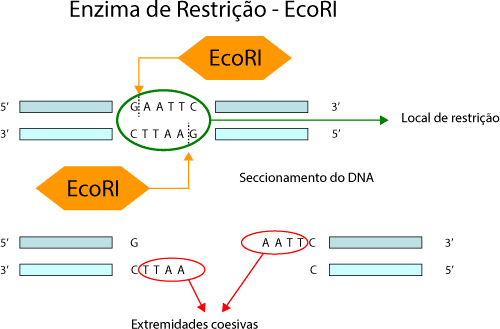
A partir desse conhecimento e isolamento dessas enzimas, por muito tempo foram utilizadas para análise de polimorfismo, ou mesmo para preparar o gene e o plasmídeo para sua posterior ligação.
Reação em Cadeia da Polimerase (PCR)
O que é?
A reação em cadeia da polimerase (PCR) é uma técnica capaz de detectar até uma cópia de DNA de qualquer célula, como o processo de extração de alguns microrganismos, por exemplo, conferem pouca presença de material genético, a PCR confere o aumento das copias de sequencias predeterminadas.
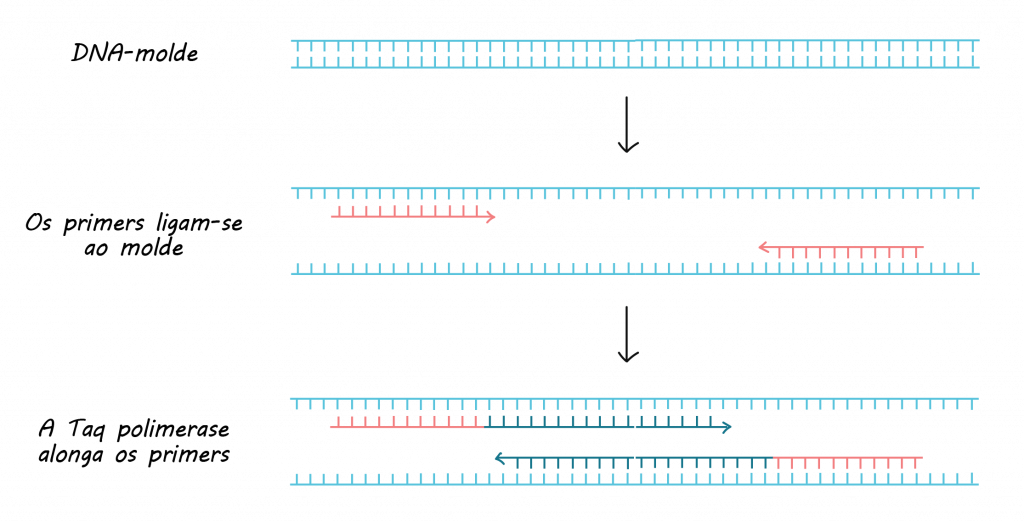
Essas sequencias predeterminadas são os primers que diante do tamanho desse oligonucleotídeo pode conferir especificidade ou não. Devido as interações que já discutimos em posts anteriores, esses primers irão se anelar em regiões que possuam sua sequência complementar – por exemplo se temos um primer:
ATTCGGCGTAAA a região complementar será:
TAAGCCGCATTT
Isso confere alta especificidade a essa técnica!
Além de alta especificidade essa técnica é sensível, e rápida, pois produzir resultados em algumas horas.
Essa amplificação específica de sequências de ácidos nucléicos através da PCR tem sido empregada no diagnóstico de inúmeras doenças infecciosas. Vários protocolos com diferentes “primers”, número de ciclos e tratamento de amostras vêm sendo desenvolvidos para o diagnóstico rápido da tuberculose e outras patologias (7).
Quem criou?
Kary Banks Mullis é um bioquímico estadunidense que se descreve como “um generalista com preconceito químico”. Além da reação em cadeia da polimerase, ele também é conhecido por ter desenvolvido um plástico que muda de cor rapidamente quando exposto à luz ultravioleta, dentre outras criações!!!
Pra que serve?
A técnica de PCR promove, por meio de etapas de variação de temperatura, a duplicação de cadeias de DNA in vitro.
A reação de amplificação de DNA por PCR envolve o emprego dos quatro nucleotídeos (dNTP’s) do DNA, sequências iniciadoras (primers) e uma DNA polimerase termoestável.
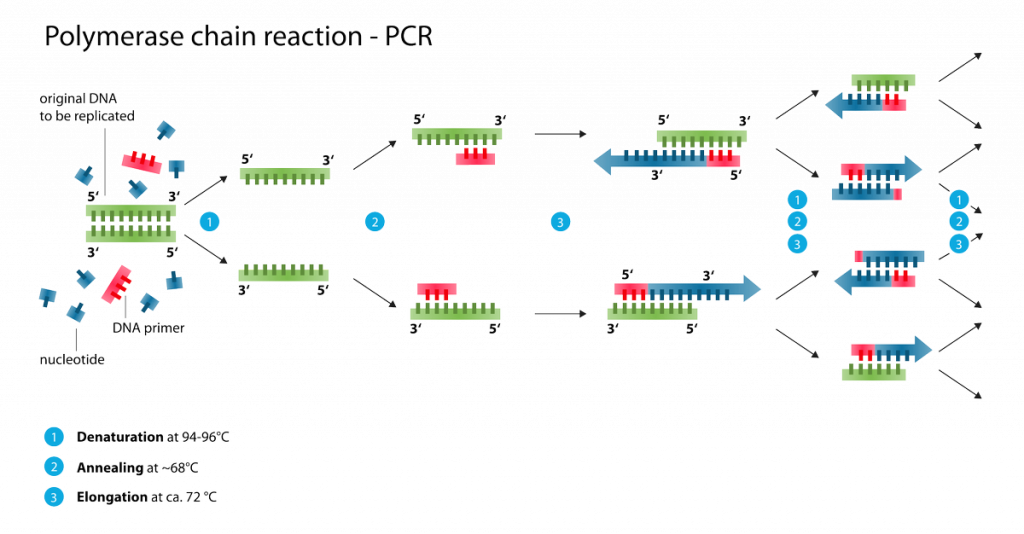
Assim, é possível a obtenção de muitas cópias de uma sequência específica de ácido nucléico, a partir de uma fita molde. Desde a introdução da técnica de PCR, rápidos avanços nas técnicas de genética molecular têm revolucionado a prática da patologia, anatomia e análises clínicas.
As técnicas moleculares são agora aplicáveis a todas as áreas do laboratório clínico.
Na anatomia patológica, apesar das análises morfológicas ainda serem a principal ferramenta de trabalho, resultados dos estudos de genética molecular têm integrado, cada vez mais, os diagnósticos nas análises cirúrgicas (8).
O que precisa ter pra funcionar?
Para que a amplificação de segmentos de DNA ocorra por PCR convencional, também denominado PCR semiquantitativo, é necessário um par de oligonucleotídeos iniciadores específicos que reconheçam o DNA que deve ser amplificado, denominado primers desoxirribonucleotídeos trifosfatados;
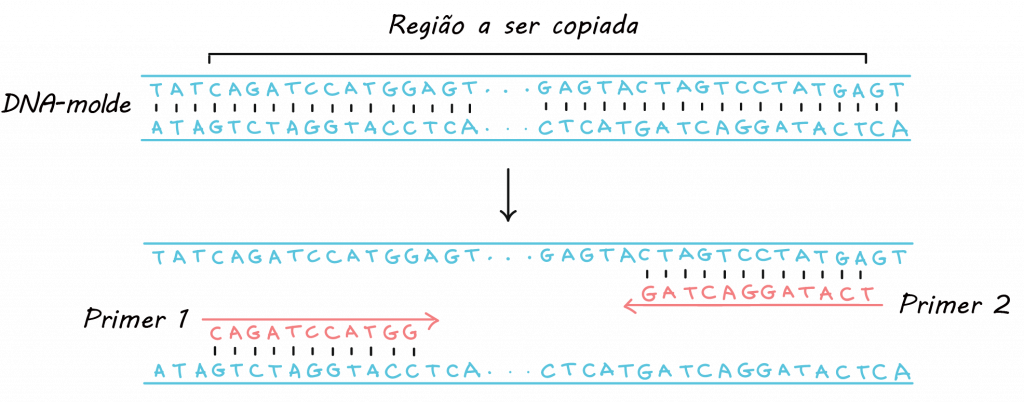
e a enzima DNA polimerase, como exemplo a Taq DNA polimerase, muito utilizada nos ensaios em laboratórios.
Os ciclos da PCR estão esquematizados na figura abaixo e são representados por desnaturação da dupla fita do DNA, por rompimento das pontes de hidrogênio, reconhecimento dos primers com o segmento específico do DNA (anelamento ou hidridização), seguido da polimerização da nova fita de DNA pela incorporação dos nucleotídeos à extremidade 3 ́ dos primers iniciadores, assim as cadeias sofrem extensão no sentido 5’- 3’.
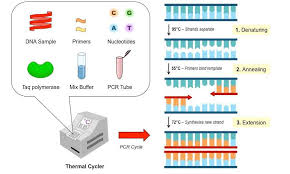
Para que esse produto de PCR e o DNA extraído relatado acima seja visualizado, utiliza-se amplamente a Eletroforese em gel, vamos aprender?
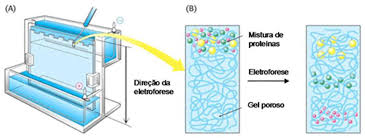
Eletroforese em gel
O que é?
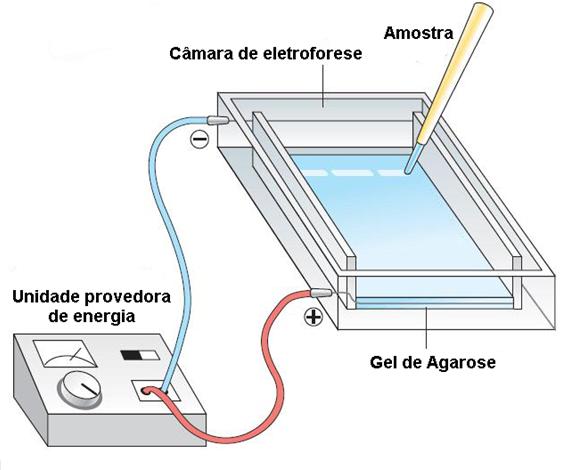
É uma técnica de separação de moléculas onde as partículas que são carregadas negativamente migram em um determinado gel durante a aplicação de uma diferença de potencial em direção a um eletrodo positivo, sendo que este é criado por uma corrente elétrica.
Para que essas amostras possam ser separadas, elas são adicionadas em um gel.
O que é gel?
Para que ocorra a realização da separação de moléculas carregadas em um campo elétrico é necessário que haja uma matriz na qual é aplicada tal amostra.
No caso da eletroforese em gel, essa função de matriz é desempenha pelo próprio gel.
Esse gel possui cavidades ou poços onde as amostras a serem analisadas serão postas e deste modo quando a corrente elétrica for ativada essas moléculas irão percorres essa matriz que possui fenestrações e que permite a separação de acordo com o peso molecular/tamanho das amostras utilizadas.
Quais os tipos de gel?
GEL DE AGAROSE: A agarose é um polissacarídeo composto por ágar e pectina. Para preparar este gel, simplesmente faz-se a mistura entre o pó de agarose e solução tampão. Diante da concentração da agarose pode se obter fenestrações maiores ou menores, que auxiliaram na visualização da amostra. Esse tipo de gel usa-se a eletroforese horizontal.
GEL DE POLIACRILAMIDA: A poliacrilamida é uma mistura de dois polímeros, acrilamida e bisacrilamida. Para preparar este gel, basta adicionar os dois polímeros nas concentrações desejadas em um suporte de vidro e na presença de um catalisador.
Esta técnica possui maior capacidade de separar fragmentos pequenos de DNA e Proteínas e que apresentam uma mínima diferença em seu peso molecular ao se comparar com o gel de agarose. Esse tipo de gel utiliza a eletroforese vertical.
Aplicação?
A eletroforese em gel de agarose é mais comumente usada na separação de moléculas de DNA e, portanto, é frequentemente usada durante técnicas de manipulação de DNA ou estudos envolvendo a identificação de indivíduos com base em sua sequência de DNA.
Para a separação das moléculas nesta técnica, temos que levar em consideração o tamanho da molécula, sendo que as de menor massa migram mais rapidamente do que as de maiores, pois possuem mais agilidade de mobilidade. Em alguns casos o formato da molécula também influencia, pois, dependendo do formato as mesmas terão mais facilidade de migrar pelo gel.
Quando se utiliza a eletroforese em gel de agarose para se visualizar e verificar a qualidade do DNA extraído, é possível visualizar apenas 1 única banda espessa e com dificuldade em migrar, visto que ali contem o DNA genômico extraído.
No entanto, quando a eletroforese em gel de agarose tem o intuito de verificar os produtos de PCR a quantidade de bandas dependerá dos primers utilizados. Caso o intuito da pesquisa seja utilização de primers inespecífico para analise polimórfica a presença de inúmeras bandas no gel com tamanhos diferentes estará no gel.
Porém se o intuito foi isolar um gene especifico utilizando primers específicos a presença de 1 única banda de interesse será o seu resultado.
Para que seja possível a determinação dos tamanhos das bandas, utiliza-se o marcador de peso molecular, um reagente que já contém fragmentos de DNA com tamanhos predeterminados.
É importante ressaltar que a eletroforese é utilizada normalmente para a separação de proteínas e moléculas de DNA e RNA. No entanto, para separação de proteínas utiliza-se mais a eletroforese vertical de poliacrilamida. O preparo das amostras de proteínas é necessário para que as cargas totais sejam anuladas e apenas ocorra a separação pelo seu tamanho.
Conclusão
Hoje aprendemos um pouco mais sobre a biologia molecular, focando na extração de DNA e RNA. Compreendemos também a importância das Enzimas de restrição, da Reação em Cadeia da Polimerase (PCR), e como a eletroforese em gel de agarose influencia diretamente no processo de extração de DNA e RNA e em sua qualidade. Assim como conhecer as técnicas de visualizar esses resultados tanto das extrações quanto em relação aos produtos de PCR e até mesmo um breve relato sobre as proteínas.
Incrível ver como a criação do PCR abriu caminho para inúmeras novas pesquisas e aplicações do DNA, sendo utilizado em laboratórios, e na biologia molecular.
Legal, ne?
Gostou? Deixe seu comentário e compartilhe com os colegas.
Até a próxima!
Referências
1. SAMBROOK. J.; RUSSEL, D. W. Molecular Cloning: A Laboratory Manual. 3.ed. New York: Cold Spring Harbor Laboratory, 2001.
2. ABOUL-SOUD, M.A.M. Clonagem de cDNA de um fator de crescimento semelhante à insulina bovina-1 de búfalos egípcios e expressão de sua proteína recombinante em Escherichia coli. Arq. Bras. Med. Veterinario. Zootec. v.72, n.2, 2020
3. MIRANDA, R.N. et al. Protocol adjustment improves the extraction of high-quality total RNA from common bean stems infected by Sclerotinia sclerotiorum. Ciênc. agrotec. v.43, 2019.
4. MULLIS, K.B. The Unusual Origin of the Polymerase Chain Reaction. Scientific American. v.262, n.4, p.56-65, 1990.
NASCIMENTO, S.; SUAREZ, E.R.; PINHAL, M.A.S. Tecnologia de PCR e RTPCR em tempo real e suas aplicações na área médica. Revista Brasileira de Medicina. 2015.
5. OLIVEIRA, C.S. et al. Detecção de proteínas imunorreativas de Rickettsia sp. cepa Mata Atlântica. Pesq. Vet. Bras. v.37, n.1, 2017.
Reiniger et al. Reciclagem de agarose em laboratórios de biologia molecular. Ciência Rural. v. 34, n.5, set-out, 2004.
6. MATSUDA, K. Chapter Two – PCR-Based Detection Methods for Single-Nucleotide Polymorphism or Mutation: Real-Time PCR and Its Substantial Contribution Toward Technological Refinement. Avanços em Química Clínica. v.80, p.45-72, 2017.
7. BOLLELA, V.R.; SATO, D.N.; FONSECA, B.A.L. Problems in the standardization of the polymerase chain reaction for the diagnosis of pulmonary tuberculosis. Journal of Public Health. v.33, n.3, p.281-6, 1999.
8. WILSON, S.M. et al. Progress toward a Simplified Polymerase Chain Reaction and Its Application to Diagnosis of Tuberculosis. Journal of Clinical Microbiology, v.31, n.4, p. 776-782. 1993.